【科研】人类细胞外囊泡miRNA表达的更新数据库
细胞外囊泡(Extracellular Vesicles, EVs)来源的miRNA作为细胞间通讯的关键介质,已在多种生理过程及疾病发生发展中被证实具有重要调控功能。然而,当前已建立的EV miRNA相关数据库普遍存在数据更新滞后、样本来源多样性有限以及整合分析工具匮乏等问题,限制了该领域的深入探索与应用转化。
近期,四川大学华西医院郭安源/雷倩团队在Nucleic Acids Research发表了题为“EVmiRNA2.0: an updated database for miRNA expression in
comprehensive human extracellular vesicles”的研究论文,该研究推出 EVmiRNA2.0 (http://guolab.wchscu.cn/EVmiRNA2.0),这是一个更新且显著扩展的资源,具有丰富的数据和增强的功能。四川大学华西医院郭安源教授和雷倩副研究员为共同通讯作者,四川大学华西医院博士后谢贵燕、博士研究生宋丹丹和罗涛为并列第一作者。

EVmiRNA2.0整合了来自45种来源、143类疾病的7,254个EVs小RNA测序样本。与上个版本EVmiRNA相比,EVmiRNA2.0主要有以下改进:(i)样本量从462个扩展到7,254个,数据量提升了15倍;(ii)新增了在线差异表达分析功能,可根据project、EV subtype、sample source 或 disease stage/treatment 灵活筛选与比较;(iii)增强的miRNA检索功能,可实现跨组织、跨体液与跨细胞类型的miRNA表达谱的检索,并融合功能注释、靶基因预测及药物交互信息等深度解析模块;(iv)支持原始表达数据和分析结果的下载。凭借其丰富的数据和用户友好的网页界面,EVmiRNA2.0将为EV领域研究者探索EVs衍生的miRNA的表达和功能提供宝贵的资源。

图1.EVmiRNA2.0的内容、架构和功能概述
一、7,000+样本集成,数据能量全面进阶
EVmiRNA2.0全新整合了7,254个人源细胞外囊泡小RNA测序数据集,涵盖371个项目、45种样本来源和143类疾病类型,是目前最全面的EV miRNA数据库(图2A)。所有样本依据来源被划分为组织、体液和细胞三大类,其中体液样本占比最高。细胞来源样本则包括原代细胞和细胞系,以干细胞和肿瘤细胞系为主(图2B,C)。此外,EVmiRNA2.0还引入了基于器官系统的疾病分类框架,便于用户在多种疾病背景下进行更具生物学意义的比较与分析。
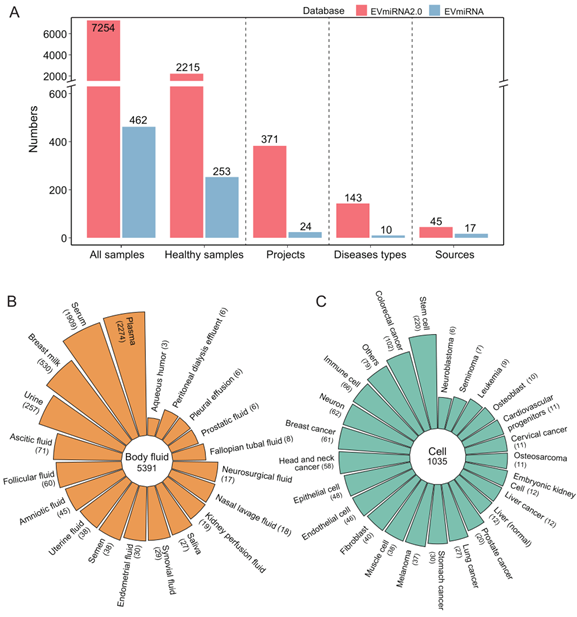
图2:EVmiRNA2.0 数据分布概览
二、在线分析+功能注释,一站式探索EV miRNA
EVmiRNA2.0新增了一站式在线差异表达分析模块,用户可在任意项目页面便捷发起分析,通过自定义分组、显著性阈值及校正方法实现灵活比较(图3)。系统将自动生成火山图、热图及差异miRNA结果表等可视化输出,帮助研究者高效识别特定条件相关的EV miRNA表达特征。EVmiRNA2.0还新增了跨来源miRNA表达谱展示功能,系统性呈现组织、体液和细胞来源EV中miRNA的平均表达水平,支持用户进行跨来源对比与特定条件下的表达模式探索。此外,数据库在每个miRNA页面整合了功能注释、TCGA泛癌表达、靶基因验证及药物交互信息,助力研究者深入解析EV miRNA在多种生理与病理过程中的作用。
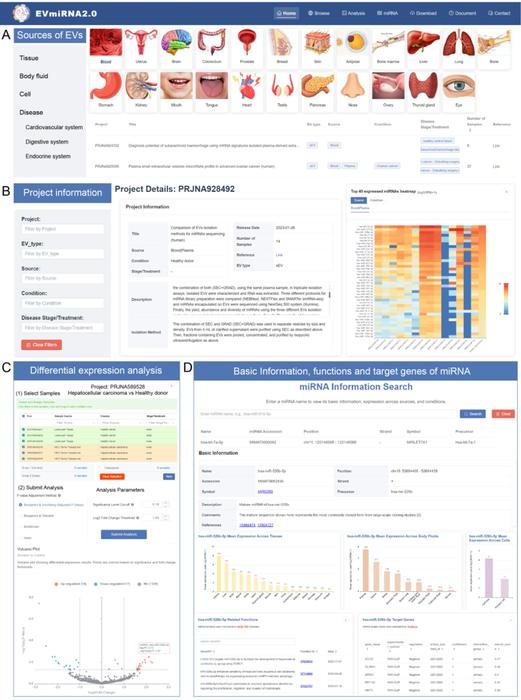
图3:EVmiRNA2.0网站界面及功能概览
参考文献:
EVmiRNA2.0: an updated database for miRNA expression in comprehensive human extracellular vesicles, Nucleic Acids Research, 2025, gkaf1054, https://doi.org/10.1093/nar/gkaf1054
外泌体之家
展源
何发
热点文章
-
【新旧版标准对比】CNAS-GL012:2025发布
2026-02-10
-
提效增能·创新提质 色谱质谱助力食品安全技术能力建设
2026-03-24
-
HJ 166-2026 土壤环境监测技术规范
2026-03-03
-
烟花爆竹中的化学知识!
2026-02-11
-
液质联用仪(LC-MS/MS)食品安全分析方案核心亮点
2026-03-20
-
【收藏】 危险化学品的安全管理
2026-01-27
-
【即将实施】2026年3月实施的食品相关标准汇总
2026-02-28
-
独立百天,新生启航:Solstice Advanced Materials中国首秀,锚定先进计算、可持续发展、生命科学新航道
2026年1月末,距离从霍尼韦尔正式分拆独立,并在纳斯达克挂牌上市将满百日时,全新的特种材料公司 Solstice Advanced Materials在上海举办了其独立运营后的首次中国媒体见面会。
作者:张明
-
安捷伦在中国:加速本土创新与绿色发展的双重推进
-
洞察未来,共谋发展 “ 数·智·未来 ” 安捷伦未来 媒体圆桌会成功举办
-
食品检验理化常用国家标准与要点
-
水分测定方法开发研究&检测相关问题故障分析解决解读
-
药物常用的晶型表征方法









评论
加载更多